近期,路运才教授课题组联合中国农业科学院作物科学研究所玉米种质资源团队在Journal of Integrative Agriculture(《农业科学学报(英文)》,JIA)上发表了题为“Leveraging disease-resistant gene mining to enhance genomic predictability for southern leaf blight in maize”的研究论文(https://www.sciencedirect.com/science/article/pii/S2095311926001115)。硕士研究生赵有裕为论文第一作者。
该研究通过大规模群体的全基因组关联分析解析了玉米抗小斑病的遗传基础,并建立了基于功能标记位点的全基因组选择高效策略,为玉米抗病育种提供了可应用的分子标记与技术支撑。
1群体结构与表型多样性分析
通过Admixture、t-SNE、进化树等分析,将玉米自交系划分为11个类群。小斑病抗性在不同类群间差异明显,其中PB类群抗性最强,SS类群最感病(图1)。热带种质类群不仅表型变异范围最广,且拥有最高的核苷酸多样性(π=0.332),表明其蕴藏丰富的抗性遗传变异。群体遗传分析进一步发现,热带种质类群与PB类群间遗传分化较低,且检测到从热带种质类群到PB类群的显著基因流。根据这一结果推测热带种质可能是小斑病抗性基因的重要供体。

图1玉米自交系群体结构与多样性分析
2全基因组关联分析和单倍型分析
研究采用多模型全基因组关联分析(GWAS),共鉴定出325个与小斑病抗性显著关联的QTN,根据LD区间将其合并为147个QTL,并明确了83个抗病候选基因(图2)。上述候选基因显著富集于植物免疫应答相关功能,包括植物-病原互作、MAPK信号及植物激素信号转导等关键通路。这些候选基因中含有已知的玉米抗病基因ChSK1与ZmMM1,其抗病优异等位基因在各类群中普遍存在,表明其已在育种中被选择利用。而新发现的抗病候选基因ZmCNGC2和ZmAGC1.8,其优异等位基因仅存在于个别类群,在当前育种材料中尚未被充分利用。

图2玉米小斑病抗性的全基因组关联分析
3全基因组选择分析
基于挖掘到的抗病候选基因,开发了一套包含83个标签SNP的标记集合,在交叉验证中达到了与完整标记集合(24,835个SNP)相当的预测精度,且该标记集合的预测能力显著优于随机标记组合(图3)。此外,在独立验证中还发现非参数模型(SVM、LightGBM)表现出更强的稳健性。值得注意的是,通过将群体结构(Q矩阵)作为协变量进行校正,标签SNP标记集合的预测性能得到显著提升,在训练集中甚至优于完整标记集合,证明基于候选基因标记的全基因组选择可作为玉米抗病分子育种的有效工具。
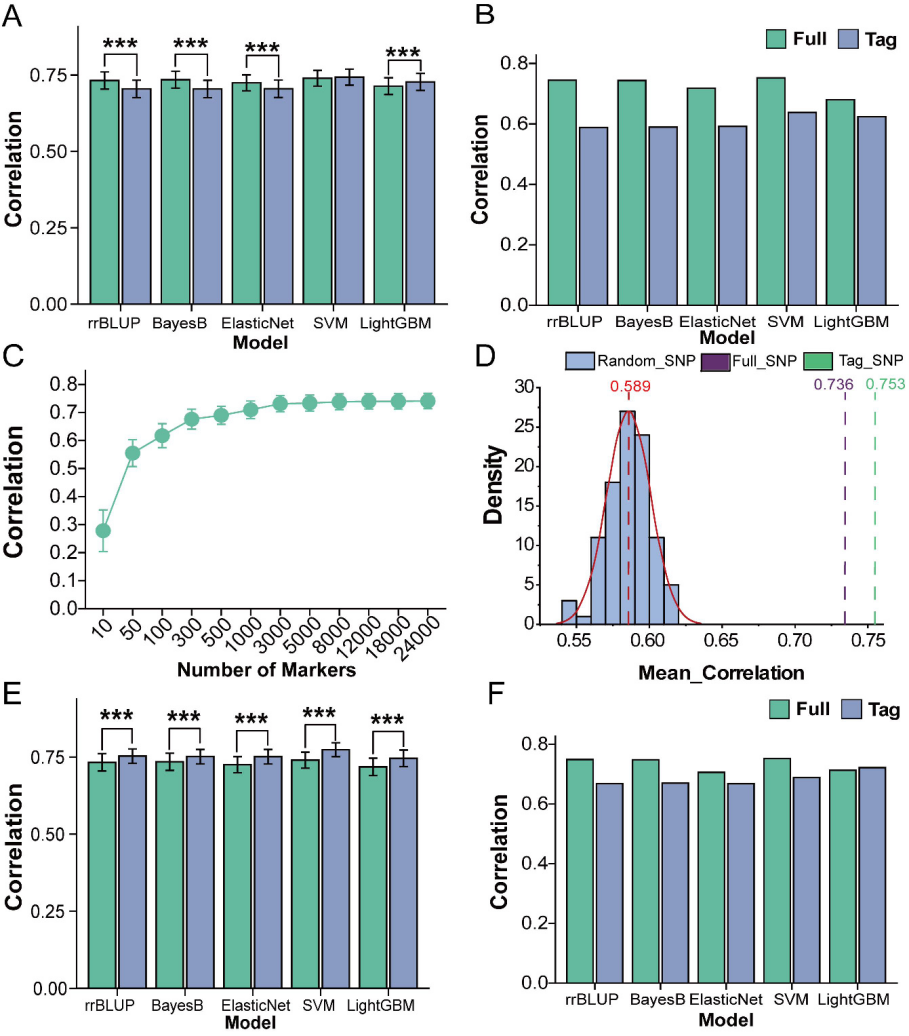
图3玉米小斑病抗性的全基因组选择分析
该研究深入解析了玉米小斑病抗性的遗传基础,建立了基于少数候选基因的全基因组选择策略,为玉米抗病分子育种提供了一个高效、实用的分子标记和工具平台。
Journal of Integrative Agriculture(《农业科学学报(英文)》, JIA)由中华人民共和国农业农村部主管,中国农业科学院与中国农学会主办,属于综合性英文学术期刊,创刊于2002年,现任主编为中国科学院院士陈化兰。JIA主要栏目有作物科学、园艺、植物保护、动物科学、动物医学、农业生态环境、食品科学、农业经济与管理等。刊稿类型有综述、研究论文、简报以及评述等。全部论文在Elsevier-ScienceDirect (SD)平台OA出版。最新SCI影响因子4.4,位于SCI-JCR农业综合学科Q1区。中国科学院分区农林科学1区。(现代农业与生态环境学院供稿)